Federico Tubaro 12 aprile 2020
Nuovo virus o RNA umano sconosciuto?
· TUTTI
PREMESSA: Per isolamento di un virus si intende la sua purificazione, ovvero separare i suoi virioni dal resto del materiale cellulare. Due metodi classici sono utilizzati per purificare i virus. Uno è basato sull’ ultrafiltrazione, l’altro sull’ultracentrifugazione. Il primo metodo consiste nel filtrare il materiale biologico prelevato dal paziente tramite filtri di porosità estremamente fine, bloccando così le particelle al di sopra di una certa dimensione. Il secondo metodo utilizza la centrifugazione a grande velocità che permette la sedimentazione del preparato in diversi gradienti che dipendono dalla densità degli elementi che li compongono. Poiché il materiale trovato con i due metodi suddetti, ha densità praticamente identica (1,16 g/ml) alle varie vescicole cellulari normalmente presenti nel citoplasma, controllare l’assenza di detriti cellulari tramite il microscopio elettronico è una necessità assoluta per poter dire di aver analizzato il virus e non del materiale appartenente alle cellule del “paziente”.
Nello studio pubblicato riguardo alla metodologia di rilevazione con real time RT-PCR del nuovo coronavirus dal titolo “Detection of 2019 novel coronavirus (2019-nCoV) by real-time RT-PCR” (https://www.ncbi.nlm.nih.gov/pmc/articles/PMC6988269) risulta chiaramente l’intento dichiarato dello studio che è il seguente: “We aimed to develop and deploy robust diagnostic methodology for use in public health laboratory settings without having virus material available”. Traduzione: “Abbiamo mirato a sviluppare e implementare una solida metodologia diagnostica da utilizzare in ambienti di laboratorio di sanità pubblica senza disporre di materiale virale”. Pare quindi che la “solida metodologia diagnostica” utilizzata in questi mesi da tutti i laboratori del mondo, può essere eseguita senza disporre di materiale virale (?!).
Nello studio sopra citato, si dice inoltre: “A viral genome sequence was released for immediate public health support via the community online resource virological.org on 10 January Wuhan-Hu-1, GenBank accession number MN908947 (https://www.ncbi.nlm.nih.gov/nuccore/MN908947 )” ovvero “Il 10 gennaio è stata rilasciata una sequenza di genoma virale per il supporto immediato della salute pubblica tramite la risorsa online della comunità virological.org“. Questa prima sequenza nominata “MN908947”, è una catena di 29903 basi di RNA a singolo filamento (ss-RNA) trovata a partire dal campione biologico identificato col nome “Wuhan-Hu-1”.
E’ importante a questo punto chiedersi se prima del sequenziamento sia avvenuto l’isolamento del virus con le modalità descritte nella premessa. Possiamo capirlo leggendo la pubblicazione riguardante lo studio del virus che sarebbe stato individuato nei primi tre pazienti di Wuhan. E’ datata 20 febbraio 2020, è ad opera del China Novel Coronavirus Investigating and Research Team (composto da una ventina di scienziati cinesi) ed ha titolo “A Novel Coronavirus from Patients with Pneumonia in China, 2019”. E’ consultabile qui:https://www.nejm.org/doi/pdf/10.1056/NEJMoa2001017. In essa si afferma: “Evidence for the presence of this virus includes identification in bronchoalveolar-lavage fluid in three patients by whole-genome sequencing, direct PCR, and culture”. Ovvero: “La prova della presenza di questo virus include l’identificazione nel liquido di lavaggio broncoalveolare in tre pazienti mediante sequenziamento dell’intero genoma, PCR diretta e coltura”. Ma si dice anche: “Although our study does not fulfill Koch’s postulates, our analyses provide evidence implicating 2019-nCoV in the Wuhan outbreak”. Ovvero: “Anche se il nostro studio non soddisfa i postulati di Koch, le nostre analisi forniscono prove che implicano 2019-nCoV nell’epidemia di Wuhan”.
Quindi è stato ammesso che i postulati di Koch (che servono per stabilire se un agente microbico è patogeno) non sono stati soddisfatti.
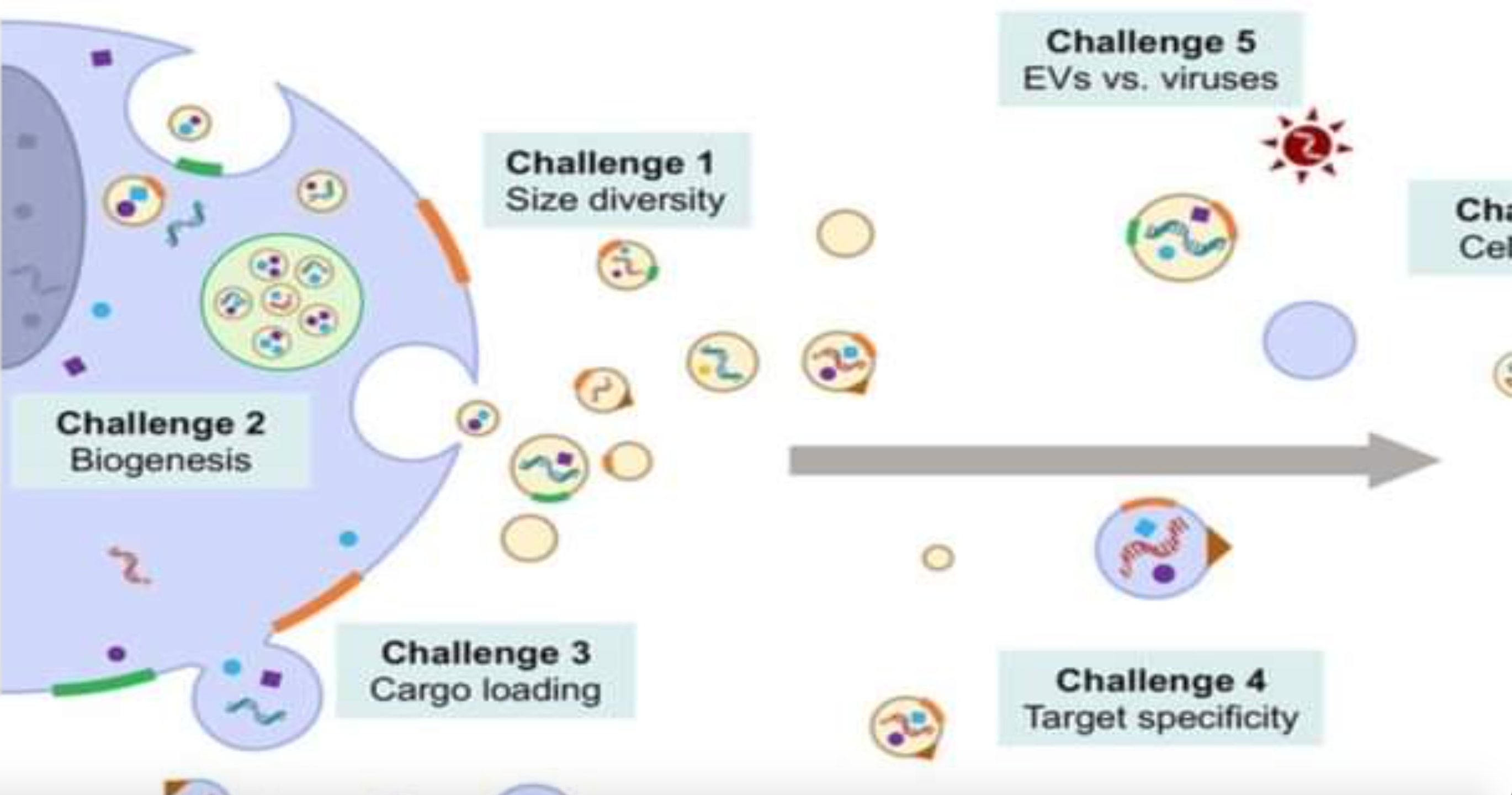
A questo punto mi viene da fare una ipotesi basata sul fatto che le EV (vescicole extracellulari) e gli RNA virus sono praticamente indistinguibili nel caso di cellula “infetta” (fontehttps://www.ncbi.nlm.nih.gov/pmc/articles/PMC4995926/pdf/pnas.201605146.pdf). Sapendo che spesso, per problemi tecnici, i virus ad RNA (Cov-2 compreso) non vengono isolati ma solo sequenziati da cellule umane, la mia ipotesi è che questa “nuova” sequenza di 29’903 basi azotate chiamata SARS-Cov-2 sia semplicemente una sequenza presente nel DNA umano (che come sappiamo è composto, se non sbaglio, da circa 6’600’000’000 basi delle quai il 97% era fino a poco tempo fa considerato “inutile”) e che corrisponda magari ad una funzione delle cellule espressa da un certo tipo di vescicole cellulari che si attivano fisiologicamente nelle forme di sofferenza polmonare con meccanismi ancora poco noti.
In sostanza, per concludere, a me pare plausibile, in linea generale, che la provenienza dei cosiddetti virus sia endogena. Se è così, per individuare il SARS-Cov-2, potrebbe essere stata ideata una procedura di RT-PCR (Reverse Transcriptase Polymerase Reaction) che permette di estrarre dal DNA umano una particolare sequenza di basi azotate che si pensa caratteristica di un nuovo virus proveniente dall’esterno, ma che in realtà corrisponde ad una delle tante funzioni biologiche a noi sconosciute e codificate nel DNA delle nostre cellule.
F.T.
Illustrazione tratta da:
Margolis L, Sadovsky Y (2019) “The biology of extracellular vesicles: The known unknowns”. PLoS Biol 17(7): e3000363. https://doi.org/10.1371/journal.pbio.3000363